- Forschung & Instrumente
- Wie wir forschen - Unsere Instrumente und Methoden
Wie wir forschen - Unsere Instrumente und Methoden
≈60 Wochen
So lange war „Tramper“ schon allein auf sich gestellt unterwegs. In mehreren tausend Metern Tiefe auf dem Meeresgrund ausgesetzt, bewegt sich der Roboter langsam vorwärts und misst regelmäßig den Sauerstoffgehalt im Meeresboden. Die Werte liefern Informationen über die Stoffkreisläufe vor Ort: Mikroorganismen zersetzen organisches Material aus den Resten abgestorbener Pflanzen und Tiere. Je mehr des organischen Materials aus oberen Wasserschichten herabsinkt, desto mehr Sauerstoff wird gezehrt.
>1 Jahr
Gut Ding will Weile haben. So ist das oft auch bei Forschungsgeräten. Zum Beispiel hat es viele Mitarbeitende und mehr als ein Jahr gebraucht, bis „Lance-A-Lot“ einsatzbereit war. Und immer noch wird dieses Gerät von uns weiterentwickelt und angepasst.
20 bis 50 Mikrometer
Haargenau messen: Unsere nadelähnlichen Mikrosensoren sind meist feiner als ein menschliches Haar. Mit den extrem dünnen Glaskapillaren können wir die Bedingungen auf kleinstem Raum und in unmittelbarer Umgebung eines einzelnen Bakteriums untersuchen. Damit die Sensoren auch perfekt zu unseren wissenschaftlichen Fragen passen, bauen wir sie meistens selbst.
Tausende Kilogramm
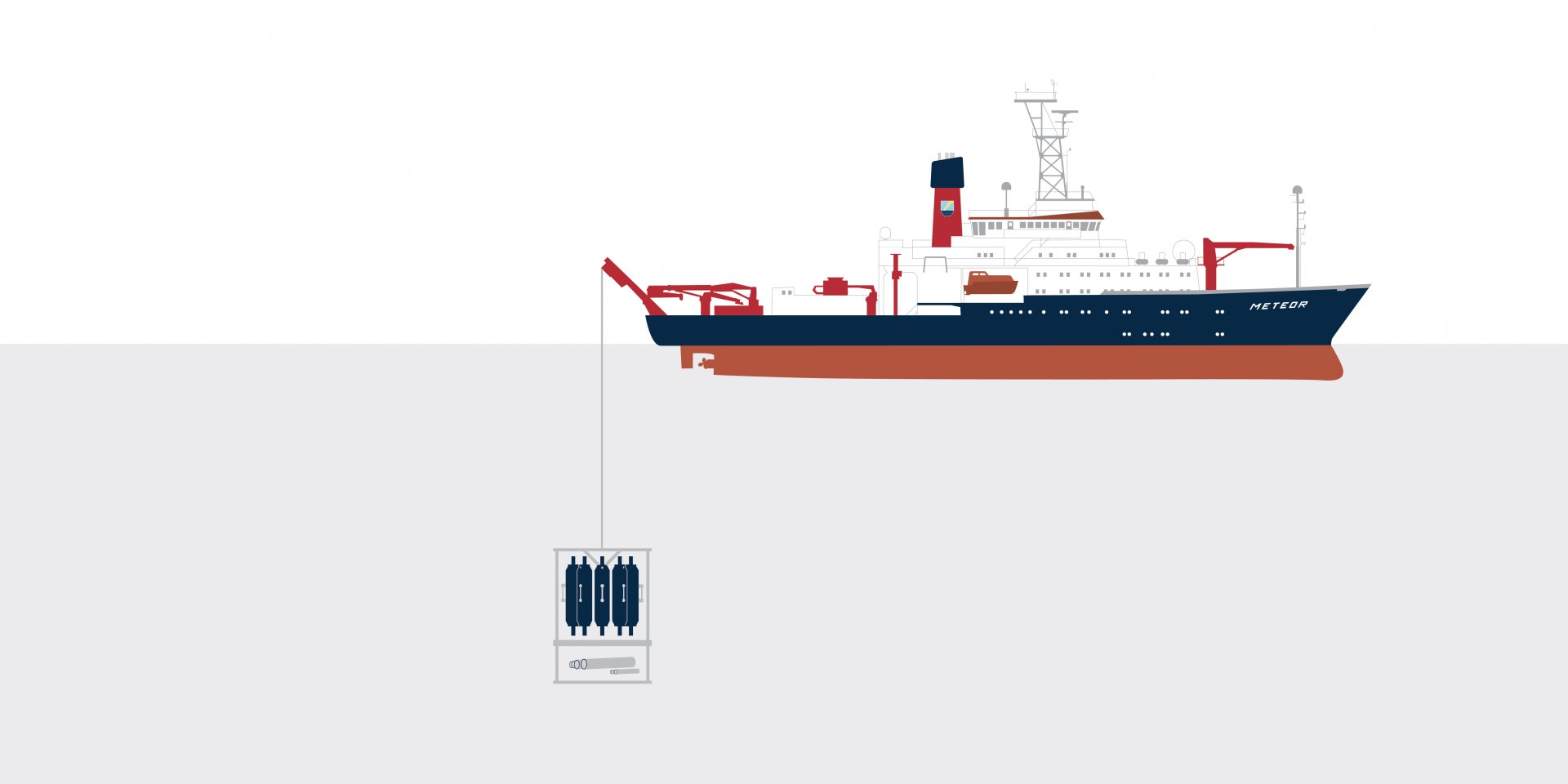
Wie kommt ein Forschungsgerät sicher vom Schiff ins Wasser und bis auf den Meeresboden? Zum Beispiel an einem starken Kabel. Und das ist selbst ein Schwergewicht: Ein 1,8 Zentimeter dickes Kabel wiegt 1,2 Kilogramm pro Meter. Das läppert sich: Um den Grund eines Tiefseegrabens zu erreichen, müssen wir schon mal fast 10.000 Kilo Kabel zu Wasser lassen!
Unsere Forschungsausstattung
Am Max-Planck-Institut für Marine Mikrobiologie nutzen wir viele verschiedene Geräte - vom einfachen Eimer über gängige Lichtmikroskope bis hin zu hochkomplexen High-Tech-Maschinen. Ein Alleinstellungsmerkmal des MPI in Bremen ist die breite Palette an unterschiedlichen Bildgebungsverfahren. So haben wir ein Nano SIMS, verschiedene Elektronenmikroskope und zahlreiche moderne Verfahren, um Gene und Genome zu analysieren. Alles unter einem Dach.
Hier geht es zur Übersicht über unsere Forschungsgeräte und -methoden: Technik & Methoden
Tiefer forschen dank Technik: Das Ende der Ozeane, der schmale Küstenstreifen, unmittelbar erlebbarer Kontaktpunkt zwischen Meer und Land, ist nur einer der vielen verschiedenen Lebensräume für Mikroben, die wir erforschen. Um die Mikrowelt auf dem offenen und auch tiefen Ozean zu erreichen, brauchen wir das größte Stück unserer Ausrüstung: Schiffe bringen uns bis zum jeweiligen Forschungsort. Auch Proben und Messdaten bekommen wir nur mit ausgefeiltem Gerät. Und haben wir dann Testtropfen Wasser und Mustermengen an Sediment, gilt es, die einzelnen Mikroorganismen darin und – noch viel diffiziler – deren innere Strukturen sichtbar zu machen.
Unsere Herausforderung ist also nicht nur die Forschung selbst, sondern stets auch, wie sie am besten gelingen kann. Neue Geräte und Technologien dafür zu entwerfen, zu bauen und weiterzuentwickeln, gehört deshalb untrennbar zu unserer wissenschaftlichen Arbeit dazu.
Lance-A-Lot: Ganz schön vermessen
Wie der sagenhafte Ritter aus König Artus’ Tafelrunde hat „Lance-A-Lot“ besondere Kräfte: Er misst gleichzeitig die Strömungsgeschwindigkeit, die Form des Meeresbodens und den Sauerstoffgehalt im Sand. Bei Rippeln etwa können Sauerstoff und Nährstoffe tiefer ins Sediment dringen als bei glatter Oberfläche. Die unter Rippeln ansässigen Mikroorganismen sind so besser versorgt. Die Strömungsgeschwindigkeit wiederum beeinflusst, was und wie viel die Bakterien im Sand veratmen und was im Wasser übrig bleibt.
Super Zoom: Einblick jenseits der Auflösung
Die meisten Mikroben entziehen sich dem bloßen Auge. Da hilft das Mikroskop, damit können wir einzelne Zellen sehen. Aber wir wollen es noch genauer wissen. Mit hochauflösenden Mikroskopen erkennen wir sogar die Strukturen im Zellinneren eines Mikroorganismus. Selbst einzelne Gene werden mit der richtigen Technik sichtbar! Diese Objekte liegen an der Auflösungsgrenze – dem Abstand, den zwei Dinge mindestens haben müssen, um optisch noch getrennt wahrnehmbar zu sein. Dafür gibt es technische Tricks: Beispielsweise können wir fluoreszierende Moleküle in den Zellen zum Blinken bringen. Durch anschließende Berechnungen am Computer entsteht ein Bild, das uns zeigt, wo genau sich die einzelnen Moleküle in einer Probe befinden. So können wir Zellstrukturen etwa fünf- bis zehnmal genauer abbilden als mit herkömmlicher Fluoreszenzmikroskopie allein.
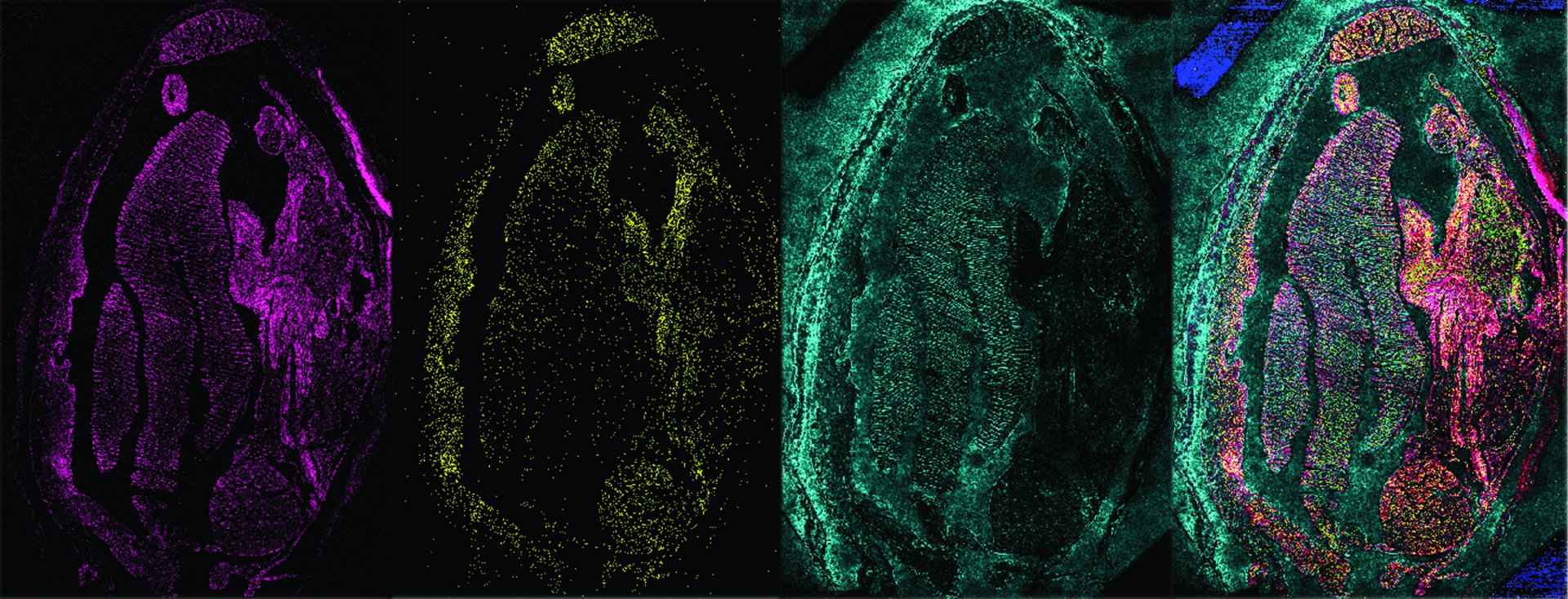
FISH: Individuen identifizieren
Mikroorganismen kann man ihrem Aussehen nach kaum unterscheiden. Dennoch hat jede Zelle ihren eigenen Fingerabdruck, der typisch für jede Art ist – das Erbmaterial. Ein Fall für FISH, die „Fluoreszenz-in-situ-Hybridisierung“. Sie macht bestimmte Abschnitte des Erbmaterials einzelner Zellen sichtbar. Unter dem Mikroskop werden diese Zellen dann zum Leuchten gebracht. FISH-Bilder von Mikroorganismen sehen aus wie ein Sternenhimmel, nur in verschiedenen Farben. Unsere Frage ist: Was erstrahlt wo? Mittels FISH können wir die Organismen in unseren Proben genau identifizieren.
NanoSIMS: Punktgenau betrachtet
NanoSIMS steht für „Nanoscale Secondary Ion Mass Spectrometre“. Dieses Massenspektrometer hat eine besondere Optik, die eine enorme räumliche Auflösung schafft: Wir können damit Dinge beobachten, die 50 Nanometer winzig sind – also ein Zwanzigstel eines Millionstel Meters. Zum Beispiel untersuchen wir so die Strukturen und Vorgänge in einer einzelnen Zelle, sehen ihr quasi beim Arbeiten zu. Das ist nahezu einmalig: Weltweit gibt es nur etwa 40 solcher Geräte. Unseres war das erste, das zur Beantwortung ökologischer Fragen eingesetzt wurde.
Bioinformatik: Meer Wissen
Mit Hilfe der Bioinformatik gewinnen wir spannendes Detailwissen über einzelne Mikroben, aber auch ganze Ökosysteme. Das Erbmaterial von Mikroben, die DNA, birgt viel Information über deren Lebensstil und Fähigkeiten. Um die DNA zu untersuchen, müssten wir die Winzlinge im Labor züchten und untersuchen – nur klappt das bei den meisten Mikroorganismen nicht. Daher analysieren wir Umweltproben mit allen Mikroben, die sich darin befinden. Ein großer Mischmasch! Dank Bioinformatik behalten wir den Überblick: Wir analysieren beispielsweise kurze Stücke der DNA-Stränge und setzen diese dann am Computer zu langen Sequenzen zusammen. So lassen sich sogar komplette Genome einzelner Arten rekonstruieren.

HyperDiver: Riffe kartieren
Korallenriffe sind wunderschön – und sehr empfindlich. Um sie zu schützen, müssen wir sie kennen und ihren „Gesundheitszustand“ ermessen. Aber wie geht das? Mit unserem HyperDiver. Er nutzt die Farben der Korallen: Je nach Art und Zustand ist ihr Farbspektrum ein anderes. Der HyperDiver „überwacht“ ein breites Spektrum an Wellenlängen – viel mehr, als das menschliche Auge sehen kann – und registriert so den Zustand des Riffs. Eine Bilderkennung und selbstlernende Software werten die Daten aus. Ein Taucher kann so bis zu 40 Quadratmeter Riff pro Minute zentimetergenau erfassen. Ein Spin-off-Team von unserem Institut hat diese Technologie nutzerfreundlich umgewandelt, das Ergebnis wird derzeit kommerzialisiert (hier geht es zu dem Start-up aus dem Max-Planck-Institut, PlanBlue).
Massenspektrometrie: Dem einzelnen Molekül auf der Spur
Beim Zusammenleben von Mikroben miteinander oder mit Tieren dreht sich alles um Moleküle. Von der Ernährung bis hin zur Kommunikation, fast immer sind Proteine, Lipide und ähnliches im Spiel. Wir machen diese Moleküle sichtbar und erlangen Einblicke in die Vorgänge innerhalb von Zellen und zwischen Zellen. Unser MALDI-MSI kann beispielsweise die Verteilung Tausender Molekülarten darstellen – ohne, dass wir diese vorher anfärben oder markieren müssen. Dieses Molekularmikroskop nutzt dazu die Molekülmasse der einzelnen Substanzen. Aus den Daten erstellen wir dann Bilder, aus denen wir erkennen, welcher Stoff wo und wie häufig vorhanden ist. Andere Massenspektrometer nutzen Isotope, das sind unterschiedliche Formen desselben Elements. Das Verhältnis der Isotope von Kohlenstoff verrät uns zum Beispiel viel über die mikrobielle Aufnahme von Kohlendioxid – und damit auch über den weltweiten Kohlenstoffkreislauf.